Portfolio Andrea Clemente
👩🔬 Andrea Clemente-Ureña 👩🔬 Andrea Clemente-Ureña
Aquí comparto mi trayectoria en biología, bioinformática y en el desarrollo de sistemas de fenotipado de alto rendimiento mediante robótica e inteligencia artificial, con énfasis en visión computacional 3D. I share my background in biology, bioinformatics, and the development of high-throughput phenotyping systems using robotics and artificial intelligence, with a focus on 3D computer vision.
Investigadora predoctoral en la Universidad Politécnica de Madrid (UPM) y el Centro de Recursos Fitogenéticos (CRF) del Instituto Nacional de Investigación y Tecnología Agraria y Alimentaria (INIA), parte del Consejo Superior de Investigaciones Científicas (CSIC).
Proyecto: Transformación digital de las actividades de conservación y mejora vegetal mediante fenotipado de alto rendimiento (HTP).
PhD researcher at the Technical University of Madrid (UPM) and the Center for Plant Genetic Resources (CRF) at the National Institute for Agricultural and Food Research and Technology (INIA), which is part of the Spanish National Research Council (CSIC).
Project: Digital transformation of plant genetic resource conservation and crop improvement activities through high-throughput phenotyping (HTP).
¡Bienvenid@ a mi portfolio! Welcome to my portfolio!

Actualmente desarrollo herramientas avanzadas para el fenotipado de alto rendimiento (HTP) aplicado a cultivos y a la caracterización estructural de plantas, utilizando Deep Learning y análisis computacional de rasgos fenotípicos.
¡Haz clic en las imágenes para ver mis proyectos!
I currently develop advanced tools for high-throughput phenotyping (HTP) applied to crop analysis and plant structural characterization, using Deep Learning and computational analysis of phenotypic traits.
Click on the images to explore my projects!
🧠 Leer sobre mi autorreflexión 🧠 Read about my self-reflection
💡 Mi primer contacto con la investigación 💡 My first encounter with research
Mi primer contacto con la investigación fue en 1º de Bachillerato en el IES Alameda de Osuna, donde desarrollé un proyecto sobre la síntesis de bioplásticos a partir de leche de vaca en las asignaturas de Biología y Técnicas Experimentales en Ciencias. Ese mismo año participé en el Finde Científico con el proyecto “De la magia del arco iris al modelo de Bohr”, formando parte de un equipo dedicado a la divulgación científica mediante experimentos de química visual.
El Finde Científico es una feria organizada por la Fundación Española para la Ciencia y la Tecnología (FECYT) y el Museo Nacional de Ciencia y Tecnología (MUNCYT), con la colaboración de Obra Social “la Caixa”.
My first experience with research took place during the first year of Bachillerato (upper secundary education) at IES Alameda de Osuna, where I developed a project on the synthesis of bioplastics from cow’s milk in Biology and Experimental Science Techniques. That same year, I took part in the Finde Científico with the project “De la magia del arco iris al modelo de Bohr”, as part of a team focused on science outreach through visual chemistry experiments.
The Finde Científico is a science fair organized by the Spanish Foundation for Science and Technology (FECYT) and the National Museum of Science and Technology (MUNCYT), with support from Obra Social “la Caixa”.


🚀 Proyectos destacados 🚀 Featured Projects

Mi tesis doctoral se centra en el desarrollo de un sistema de fenotipado vegetal de alto rendimiento mediante robótica autónoma, visión computacional 3D e imagen hiperespectral. Trabajo con datos obtenidos de cámaras RGB e hiperespectrales para entrenar modelos de inteligencia artificial que permitan reconstrucciones 3D, segmentación de estructuras vegetales y detección de estrés.
Colaboro activamente con el Centro de Automática y Robótica (CAR, CSIC-UPM) y la empresa tecnológica INYCOM en el marco del contrato predoctoral MOMENTUM MMT24-PTI AGROFOR.
En 2025 participé en la escuela de verano de inteligencia artificial organizada por AIHUB-CSIC en Zaragoza, donde presenté el póster titulado “IA y visión 3D hiperespectral para fenotipado de alto rendimiento” DOI: 10.13140/RG.2.2.27077.77289.
My PhD research focuses on developing a high-throughput plant phenotyping system using autonomous robotics, 3D computer vision, and hyperspectral imaging. I work with RGB and hyperspectral data to train AI models for 3D reconstruction, plant structure segmentation, and stress detection.
I actively collaborate with the Centre for Automation and Robotics (CAR, CSIC-UPM) and the tech company INYCOM, within the framework of the MOMENTUM MMT24-PTI AGROFOR predoctoral contract.
In 2025, I participated in the summer school on artificial intelligence organized by AIHUB-CSIC in Zaragoza, where I presented the poster titled “AI and 3D Hyperspectral Vision for High-Throughput Phenotyping” DOI: 10.13140/RG.2.2.27077.77289.
He adquirido experiencia en el análisis computacional de datos ómicos, aplicando técnicas de bioinformática, estadística y programación con R y Python para interpretar información transcriptómica, genómica y epigenética. Utilizo métodos como análisis de expresión diferencial, clustering, enriquecimiento funcional y visualización de datos.
En mi Trabajo Final de Máster, realicé un estudio sobre la identificación y caracterización de fragmentos derivados de ARN de transferencia (tRFs) sobreexpresados en un modelo murino de la enfermedad de Huntington. Los tRFs son pequeñas moléculas de ARN emergentes con funciones regulatorias potenciales. Utilicé datasets reales de RNA-seq proporcionados por el grupo de investigación liderado por Eulàlia Martí y con la tutoría de la Dra. Geòrgia Escaramís (Universitat de Barcelona). Analicé datos transcriptómicos de tejido cerebral de ratón, aplicando pipelines bioinformáticos para detectar tRFs diferencialmente expresados, inferir su posible función y vincularlos con rutas biológicas relevantes en el contexto de Huntington. Este trabajo aporta información sobre posibles biomarcadores o mecanismos moleculares implicados en la progresión de la enfermedad.
TFM: Identificación y caracterización de los tRFs sobreexpresados en la enfermedad de Huntington mediante herramientas bioinformáticas. DOI:
10.13140/RG.2.2.33680.32001
I have developed experience in computational omics data analysis, applying bioinformatics, statistics, and programming in R and Python to interpret transcriptomic, genomic, and epigenetic data. I work with differential expression analysis, clustering, functional enrichment, and data visualization.
For my Master's Thesis, I conducted a study focused on identifying and characterizing transfer RNA-derived fragments (tRFs) overexpressed in a mouse model of Huntington’s disease. tRFs are small emerging RNA molecules with potential regulatory roles. I used real RNA-seq datasets provided by the research group led by Eulàlia Martí and supervised by Dr. Geòrgia Escaramís (University of Barcelona). I analyzed transcriptomic data from mouse brain tissue using bioinformatics pipelines to detect differentially expressed tRFs, assess their potential functions, and explore their involvement in biological pathways associated with Huntington’s disease. This work contributes to the understanding of tRFs as potential biomarkers or regulators of disease progression.
Master's Thesis: Identification and characterization of overexpressed tRFs in Huntington's disease using bioinformatics tools. DOI:
10.13140/RG.2.2.33680.32001
Cuento con formación sólida en genética molecular, citología y biología celular, incluyendo técnicas avanzadas de laboratorio, embriología y análisis genético en organismos modelo y no modelo. He trabajado con herramientas bioinformáticas y bases de datos genómicas para estudiar la organización y evolución de genes.
En mi Trabajo de Fin de Grado realicé una caracterización estructural exhaustiva de los genes que codifican proteínas de la subunidad mayor del ribosoma en el protista parásito Leishmania. Este trabajo se centró en analizar la organización génica, intrones, regiones UTR y conservación entre especies, empleando análisis de secuencias, anotaciones funcionales y herramientas como MEME para el estudio de motivos conservados.
El estudio se llevó a cabo bajo la dirección del Dr. José María Requena en el CBMSO (Centro de Biología Molecular Severo Ochoa, CSIC-UAM), y contribuyó a la comprensión funcional y evolutiva de la maquinaria ribosomal en kinetoplástidos, parásitos de gran relevancia biomédica.
TFG: Caracterización estructural de los genes codificantes de proteínas de la subunidad mayor del ribosoma en el protista Leishmania. DOI: 10.13140/RG.2.2.10192.21767
Participación mencionada en el Informe Científico del CBMSO-CSIC 2021–2022 .
I have a strong background in molecular genetics, cytology, and cell biology, including advanced laboratory techniques, embryology, and genetic analysis in both model and non-model organisms. I have used bioinformatics tools and genomic databases to study gene structure and evolution.
For my Bachelor's Thesis, I performed a comprehensive structural characterization of genes encoding large ribosomal subunit proteins in the parasitic protist Leishmania. The work focused on gene organization, introns, UTR regions, and interspecies conservation, employing sequence analysis, functional annotation, and tools such as MEME for conserved motif discovery.
This study was conducted under the supervision of Dr. José María Requena at CBMSO (Centro de Biología Molecular Severo Ochoa, CSIC-UAM), contributing to the functional and evolutionary understanding of ribosomal machinery in kinetoplastid parasites, which hold significant biomedical relevance.
Bachelor's Thesis: Structural characterization of genes encoding large ribosomal subunit proteins in the protist Leishmania. DOI: 10.13140/RG.2.2.10192.21767
Mentioned in the CBMSO-CSIC 2021–2022 Scientific Report .
Detección Inmunohistoquímica de BRCA en Cáncer de Mama
En este proyecto llevado a cabo en el hospital HM de Sanchinarro, realicé la detección inmunohistoquímica de los genes BRCA1 y BRCA2 en muestras de tejido mamario con sospecha de cáncer. Utilicé anticuerpos específicos para BRCA y otros marcadores como HER2, Ki-67, ER y PR. Tras aplicar los anticuerpos, se visualizó la expresión de BRCA en las células mediante un marcador cromogénico (DAB), que generó una coloración marrón característica en las células positivas.
Este proyecto me permitió desarrollar habilidades en técnicas de inmunohistoquímica, microscopía y la interpretación de marcadores tumorales en la investigación del cáncer de mama.
Immunohistochemical Detection of BRCA in Breast Cancer
In this project carried out at the HM Hospital in Sanchinarro, I performed the immunohistochemical detection of BRCA1 and BRCA2 genes in breast tissue samples with suspected cancer. I used specific antibodies for BRCA, as well as other markers such as HER2, Ki-67, ER, and PR. After applying the antibodies, the expression of BRCA in the cells was visualized through a chromogenic marker (DAB), which produced a characteristic brown staining in the positive cells.
This project allowed me to develop skills in immunohistochemical techniques, microscopy, and tumor marker interpretation in breast cancer research.

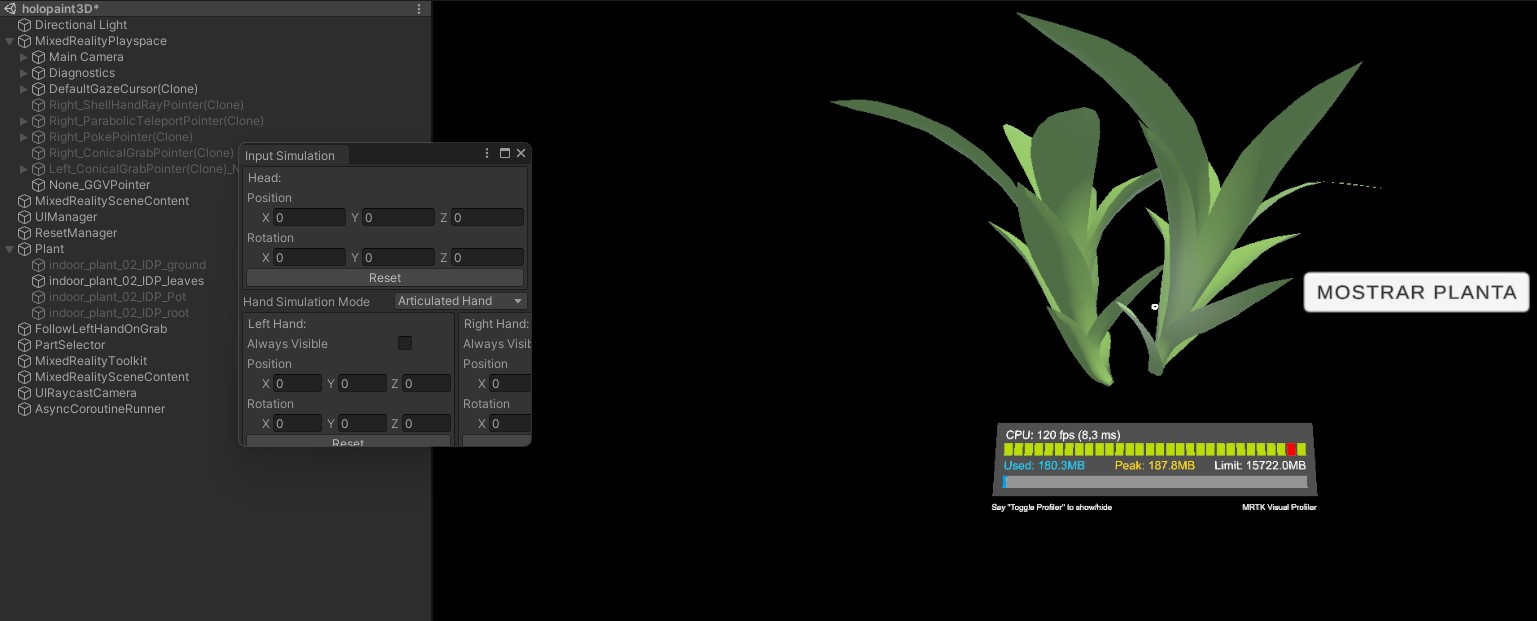
Colaboración con el Centro de Automática y Robótica (CAR-CSIC-UPM) para el desarrollo de soluciones inmersivas utilizando Microsoft HoloLens 2 en aplicaciones agrícolas. Actualmente, trabajo en un modelo 3D interactivo de una maceta virtual desarrollado en Unity con C#. Mediante la interacción manual en las gafas de realidad aumentada, el usuario puede seleccionar zonas específicas del modelo; las demás zonas desaparecen y aparece un cartel con el nombre de la zona seleccionada.
El proyecto está en fase inicial, pero se prevé integrar progresivamente inteligencia artificial para realizar segmentación y etiquetado en tiempo real basados en modelos generados a partir de nubes de puntos de plantas reales, mejorando la precisión y utilidad en entornos agrícolas.
Collaboration with the Center for Automation and Robotics (CAR-CSIC-UPM) to develop immersive solutions using Microsoft HoloLens 2 for agricultural applications. Currently, I am working on an interactive 3D model of a virtual flowerpot developed in Unity with C#. Through hand interaction in the augmented reality headset, users can select specific zones of the model; the other zones disappear and a label with the selected zone's name appears.
The project is in an early stage, with plans to progressively integrate artificial intelligence for real-time segmentation and labeling based on models derived from point clouds of real plants, enhancing accuracy and utility in agricultural environments.

🎓 Formación académica 🎓 Academic Education
-
📘 Doctorado en Automática y Robótica (2024 - actualidad)
Universidad Politécnica de Madrid – INIA-CSIC 📘 PhD in Automation and Robotics (2024 - Present)
Polytechnic University of Madrid – INIA-CSIC -
📊 Máster en Bioinformática y Bioestadística (2022 - 2024)
Universitat Oberta de Catalunya / Universitat de Barcelona 📊 Master in Bioinformatics and Biostatistics (2022 - 2024)
Open University of Catalonia / University of Barcelona -
🧬 Grado en Biología (2016 - 2021)
Universidad Autónoma de Madrid 🧬 Bachelor in Biology (2016 - 2021)
Autonomous University of Madrid -
🔬 Técnico Superior en Anatomía Patológica y Citología (2014 - 2016)
CESUR II 🔬 Higher Technician in Pathological Anatomy and Cytology (2014 - 2016)
CESUR II
🛠️ Tecnologías y herramientas 🛠️ Technologies and Tools
| LenguajesLanguages | Python • R • SQL • BASH • HTML/CSS • JavaScript • C# |
| Ciencia & BioinfoScience & Bioinformatics | Bioconductor • SPSS • Galaxy • Novopath • BLAST • Alineamientos • Análisis genómicos |
| IA / VisiónAI / Vision | TensorFlow • PyTorch • Scikit-learn • Keras • OpenCV • Pandas • NumPy • Matplotlib |
| RobóticaRobotics | Sensores RGB • Sensores Multiespectrales • Sensores LiDAR/ToF • HoloLens 2 |
| EntornosEnvironments | Linux • VS Code • Unity • GitHub • Office |
📚 Experiencia profesional 📚 Professional Experience
-
🔬 Investigadora Predoctoral | INIA-CSIC (2024 - actualidad)
Fenotipado automatizado de cultivos con robótica y visión computacional. Diseño experimental y análisis de datos fenotípicos. 🔬 Predoctoral Researcher | INIA-CSIC (2024 - Present)
Automated crop phenotyping with robotics and computer vision. Experimental design and phenotypic data analysis. -
🧫 Técnico de Anatomía Patológica | HM Hospitales (2016)
Procesamiento y análisis de muestras biológicas y técnicas histológicas. 🧫 Pathological Anatomy Technician | HM Hospitales (2016)
Processing and analysis of biological samples and histological techniques. -
📞 Teleoperadora Comercial | My Assessor Total (2021)
Primer contacto con el mundo laboral. Aprender cómo funciona el empleo fuera del ámbito científico. 📞 Commercial Operator | My Assessor Total (2021)
First contact with the working world. Learning how employment works outside the scientific field.
🌐 Idiomas 🌐 Languages
- Español: NativoSpanish: Native
- Inglés: Nivel C (APTIS - British Council)English: Level C (APTIS - British Council)
- Francés: Nivel A2 (DELF)French: Level A2 (DELF)
- Alemán: Nivel básicoGerman: Basic level
- Catalán: Nivel básicoCatalan: Basic level
🎓 Cursos 🎓 Courses
- 📘 Microcredencial Portfolio Digital (75 horas, 2025) – CSIC 📘 Digital Portfolio Microcredential (75 hours, 2025) – CSIC
- 📊 Statistics for Natural Resources ->Ejercicio final (30 horas, 2025) – UPM 📊 Statistics for Natural Resources->Final exercise (30 hours, 2025) – UPM
-
🤖 Inteligencia Artificial y Software Development ->Laboratorios (13,5 horas, 2025) – IBM y UPM
🤖 Artificial Intelligence and Software Development ->Labs (13.5 hours, 2025) – IBM & UPM


- 🌐 Conecta y colabora de forma efectiva en entornos digitales (25 horas, 2025) – CSIC 🌐 Connect and Collaborate Effectively in Digital Environments (25 hours, 2025) – CSIC
- 💻 Microsoft Certified Solutions Developer (MCSD): Web Applications (240 horas, 2021) 💻 Microsoft Certified Solutions Developer (MCSD): Web Applications (240 hours, 2021)
🗓️ Seminarios y Jornadas 🗓️ Seminars and Workshops
- 🌱 Jornada Técnica sobre Recursos Genéticos de Leguminosas: Conservación y Utilización – INIA-CSIC 2025 🌱 Technical Workshop on Genetic Resources of Legumes: Conservation and Utilization – INIA-CSIC 2025
- 🤖 Escuela de Verano AIHUB: Retos de la IA – Zaragoza 2025 – CSIC 🤖 AIHUB Summer School: Challenges of AI – Zaragoza 2025 – CSIC
- 📍 Invitación I Encuentro Momentum, 26 febrero – CFTMAT (Madrid) 2025 📍 Invitation to the First Momentum Meeting, February 26 – CFTMAT 2025 (Madrid)
- 🚀 Evento de presentación del programa Atracción y Talento – Iniciativa Generación D 2025 🚀 Program Presentation Event: Attraction and Talent – Generation D Initiative 2025
- 🎓 Jornada Microcredenciales – CSIC 2025 🎓 Microcredentials Workshop – CSIC 2025
🧠 Autorreflexión sobre mi proceso de aprendizaje 🧠 Self-reflection on my learning process
Mi primer contacto con la investigación fue en 1º de Bachillerato, cuando desarrollé un proyecto sobre la síntesis de bioplásticos a partir de leche de vaca. Aquel acercamiento despertó en mí una gran curiosidad científica y me hizo descubrir lo apasionante que es generar nuevo conocimiento. Desde entonces, he continuado profundizando en distintas áreas y cada experiencia ha reforzado mi interés por la ciencia aplicada y multidisciplinar. My first contact with research was in the first year of Bachillerato (upper secondary education), when I developed a project on the synthesis of bioplastics from cow's milk. That early exposure sparked a deep scientific curiosity and made me realize how exciting it is to generate new knowledge. Since then, I have continued exploring various fields, and each experience has reinforced my interest in applied and multidisciplinary science.
Durante el máster, adquirí conocimientos sólidos en programación con Python y R, así como en técnicas de machine learning, que me han permitido procesar y analizar grandes volúmenes de datos, y abordar problemas complejos desde una perspectiva cuantitativa. During my master's, I gained solid knowledge in programming with Python and R, as well as in machine learning techniques, which have allowed me to process and analyze large volumes of data and tackle complex problems from a quantitative perspective.
Actualmente, en mis proyectos más recientes, combino estos conocimientos con técnicas de visión por computador, robótica e inteligencia artificial aplicadas a la biología y la agricultura de precisión. Esta combinación multidisciplinar me permite trabajar con sensores avanzados y desarrollar soluciones innovadoras para el fenotipado automatizado y otras aplicaciones. Currently, in my more recent projects, I combine this knowledge with computer vision, robotics, and artificial intelligence techniques applied to biology and precision agriculture. This multidisciplinary combination allows me to work with advanced sensors and develop innovative solutions for automated phenotyping and other applications.
He mejorado significativamente en el trabajo en equipo, y durante la escuela de verano AIHub pude reforzar mis habilidades de comunicación, aprendiendo a transmitir mis ideas de forma más clara y efectiva. Aun así, sigo trabajando para optimizar la gestión del tiempo y seguir perfeccionando cómo presento mis resultados, tanto a audiencias técnicas como a personas sin formación científica. I have significantly improved my teamwork skills, and during the AIHub summer school, I was able to strengthen my communication abilities, learning to convey my ideas more clearly and effectively. Still, I continue working to optimize time management and improve how I present my results, both to technical audiences and to people without a scientific background.
De cara al futuro, me motiva seguir formándome en inteligencia artificial, realidad aumentada y robótica, especialmente dentro del ámbito de la biotecnología y la agricultura de precisión. Estoy abierta a seguir colaborando en proyectos innovadores y a perfeccionar tanto mis capacidades técnicas como mis habilidades blandas, como la comunicación, la organización y el trabajo en equipo. Looking ahead, I’m motivated to continue training in artificial intelligence, augmented reality, and robotics, especially within biotechnology and precision agriculture. I’m open to collaborating on innovative projects and improving both my technical skills and soft skills, such as communication, organization, and teamwork.
En resumen, esta reflexión me ha ayudado a tomar perspectiva sobre mi evolución reciente. Sigo comprometida con aprender, adaptarme y crecer personal y profesionalmente, con la convicción de que la investigación es una herramienta clave para impactar positivamente en el mundo. In summary, this reflection has helped me gain perspective on my recent evolution. I remain committed to learning, adapting, and growing both personally and professionally, with the conviction that research is a key tool to positively impact the world.
📫 Contacto 📫 Contact
- 📖 ResearchGate:📖 ResearchGate: Andrea-Clemente-Urena-2
- 🔗 LinkedIn:🔗 LinkedIn: linkedin.com/in/andreaclementeureña
- 💻 GitHub:💻 GitHub: andreaclemente96
